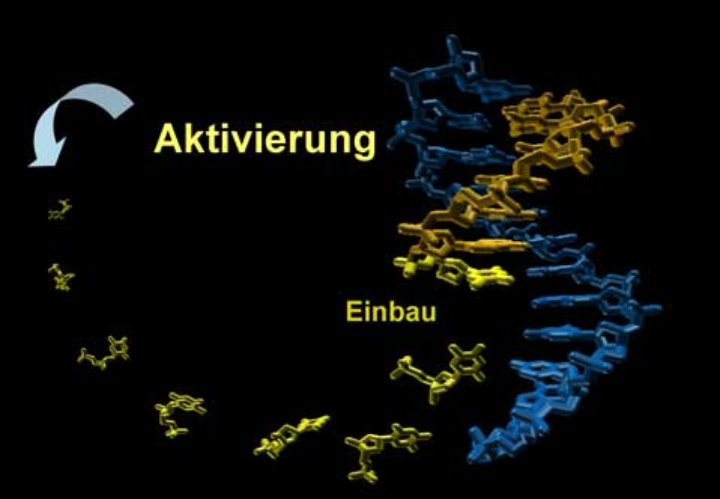
In der Natur wird die in den Genen gespeicherte Erbinformation mit Hilfe von Enzymen abgelesen. Nun ist der Nachweis gelungen, dass dieser Vorgang unter bestimmten Umständen auch ohne Enzyme effizient stattfinden kann. Bisher hatte man geglaubt, dass spontane, rein chemische Ablesevorgänge nur bei sehr wenigen Sequenzen ablaufen können, und zwar nur, wenn diese eine besonders hohe Bindungsfähigkeit für die einzelnen Bausteine der DNA haben. Dr. Eric Kervio und Prof. Clemens Richert vom Institut für Organische Chemie der Universität Stuttgart konnten in Zusammenarbeit mit Annette Hochgesand vom Karlsruher Institut für Technologie und Prof. Ulrich Steiner von der Universität Konstanz zeigen, dass solche spontanen molekularen Ablesungsvorgänge für zahlreiche mögliche Sequenzen mit großer Effizienz ablaufen. Über ihre Forschung berichtet jetzt die online-Version der Zeitschrift Proceedings of the National Academy of Sciences USA. *) Die Nutzung der Ergebnisse ist für die Entwicklung von preiswerten Sequenzierungsverfahren zur Diagnose von genetischen Veränderungen in der DNA von Patienten denkbar.
Die beiden Stränge der DNA-Doppelhelix, aus der die Gene bestehen, sind durch Basenpaare
miteinander verbunden. Dabei paaren jeweils die Kernbasen Adenin (A) und Thymin (T) sowie Guanin
(C) und Cytosin (C). Die G-C-Basenpaare sind sehr viel stärker als die A-T-Basenpaare. Zudem
beeinflussen die benachbarten Kernbasen die Bindungsstärke. Wenn zum Beispiel A von zwei weiteren
A-Nachbarn umgeben ist, wird das komplementäre T kaum noch gebunden. Von den 64 möglichen
Kombinationen aus Kernbase und den beiden Nachbarbasen galten deshalb viele als aussichtslos für
die spontane, enzymfreie Ablesung. Das Wissenschaftlerteam wies nun aber nach, dass solche
molekularen Ablesungsvorgänge für jede Abfolge von drei Kernbasen mit großer Effizienz ablaufen.
Eine geringe Erniedrigung der Temperatur auf 10 Grad Celsius und eine leicht zu induzierende
chemische Aktivierung der Bausteine genügt, damit innerhalb von wenigen Stunden ein spontaner
Einbau ohne Enzyme erfolgt. Die Unterschiede in der Reaktionsgeschwindigkeit zwischen den am besten
bindenden Sequenzmotiven und denen, die die Basen nur scheinbar schwach binden, sind kleiner als
ein Faktor von 100.
Die Ergebnisse der Arbeit zeigen die ganz besondere Eignung der DNA für ihre Rolle als
genetisches Material. „Die Hürden für einen spontanen Einbau von einzelnen Nukleotiden sind – wie
die Messungen nahe legen – niedriger, als man zuvor hätte annehmen können. Damit geraten spontane
Ablese-Vorgänge also nicht so leicht an besonders schlecht bindenden Bereichen ins Stocken“,
erklärt Prof. Clemens Richert. Die von dem Forscherteam durchgeführten Messungen beziehen sich auf
Einzelschritte, und es besteht aufgrund der notwendigen chemischen Aktivierung nicht die Gefahr,
dass von alleine neue Gene entstehen. Trotzdem eröffnen die erhaltenen Messdaten neue Szenarien für
eine mögliche Entstehung des Lebens aus einfachen, rein chemischen Ausgangsmaterialien. Gegenwärtig
werden deshalb auch Messungen an der RNA (die eng verwandt mit der DNA ist) durchgeführt, der eine
ganz besondere Rolle in der präbiotischen Chemie der frühen Erde zugesprochen werden, weil sie auch
katalytisch aktiv sein kann. Weiterhin helfen die nun erhaltenen Ergebnisse möglicherweise bei der
Entwicklung von preiswerten Sequenzierungsverfahren zur Diagnose von genetischen Veränderungen in
der DNA von Patienten.
*) Titel der Arbeit: „Templating efficiency of naked DNA”, abrufbar unter
www.pnas.org/content/early/recent.
Weitere Informationen bei:
Prof. Clemens Richert
Institut für Organische Chemie der Universität Stuttgart
Tel. 0711/685-64311
e-mail:
lehrstuhl-2@oc.uni-stuttgart.de.